R言語プログラミング: クラスター分析 - 階層的クラスタリング
第2回データマイニング+WEB勉強会@東京の「はじめてでもわかる R言語によるクラスター分析」の内容に関する、ソースコードも以下に記載します。
※記載しているソースは、R Console上や EclipseでR-Scriptとして、貼り付けそのまま実行可能です。(Rのインストール・環境設定はこちらで、RをEclipseで実行するための方法はこちら)
講義の全体内容・構成は次をご覧下さい。
・R勉強会: 第2回データマイニング+WEB 勉強会@東京 (Tokyo.Webmining) を開催しました - 「はじめてでもわかる R言語によるクラスター分析-
・Slideshare:はじめてでもわかる R言語によるクラスター分析
クラスター分析と評価
エントロピー(Entropy)と純度(Purity)の算出関数
#関数:エントロピー(Entropy)算出, ct:クロス集計表 calcEntropy <- function(ct){ -sum( (apply(ct,1,sum)/sum(ct)) * apply(ct,1,calcEntropy0))/log(ncol(ct)) } calcEntropy0<-function(pv){ p1<-pv/sum(pv) p2<-p1[p1 !=0] sum(p2*log(p2)) } #関数:純度 (Purity)算出 calcPurity <-function(ct){ sum(apply(ct,1,max))/sum(ct) }
クラスター分析の実行と評価
x <- iris[,1:4] #解析データ:iris 1-4列のデータ d <- dist(x) #距離行列の作成 hc <- hclust(d); #Clusterを求める。完全連結法"complete"(Default) op <- par(mfrow=c(1,1)) plot(hc) #デンドログラムの表示 result <- cutree(hc,3) #クラスタリング結果:3つのクラスターに分割 answer <- iris[,5] #クラスタリング正解:品種(iris 5列目) ctbl <- table(answer, result) #正解と結果のクロス表を作成 ctbl #クロス表の表示 calcEntropy(ctbl) #エントロピー(Entropy)の算出 calcPurity(ctbl) #純度 (Purity)の算出
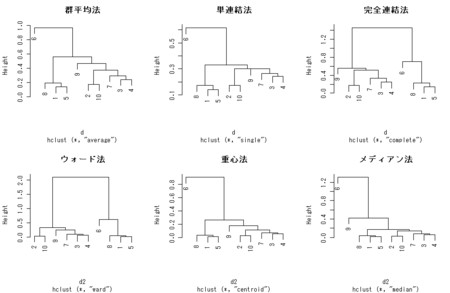
クラスター比較
#階層的クラスタリング手法 x <- iris[1:10,1:4] #解析データ:iris 1-4列のデータ 10行分(見やすさのため限定) d <- dist(x) #初期距離行列の作成:ユークリッド距離 d2 <- dist(x)^2 #ユークリッド平方距離 hc.aver <- hclust(d,"average") #群平均法 hc.sngl <- hclust(d,"single") #単連結法 hc.comp <- hclust(d) #完全連結法(Default):"complete"指定と同じ hc.ward <- hclust(d2,"ward") #ウォード法 hc.cntr <- hclust(d2,"centroid") #重心法 hc.medi <- hclust(d2,"median") #メディアン法 op <- par(mfrow=c(2,3)) #Graphic parameter設定:2行3列画面表示 plot(hc.aver, main="群平均法") plot(hc.sngl, main="単連結法") plot(hc.comp, main="完全連結法") plot(hc.ward, main="ウォード法") plot(hc.cntr, main="重心法") plot(hc.medi, main="メディアン法") par(op)#作業前のGraphic Parameterに戻す
エントロピー・純度 比較
指定数のクラスタ算出・評価 関数
#関数:クラスタリング手法 methでの、clsnum数のクラスタ を算出 calchclust <- function(x, clsnum, meth="complete"){ #methデフォルトは完全連結法("complete") d2 <- dist(x)^2 #ユークリッド平方距離 switch(meth, #初期距離行列の設定 "ward" = d <- d2, #ウォード法 の場合:ユークリッド平方距離 "centroid" = d <- d2, #重心法 の場合:ユークリッド平方距離 "median" = d <- d2, #メディアン法 の場合:ユークリッド平方距離 d <- dist(x) #デフォルト: ユークリッド距離 ) hc <- hclust(d, method = meth) #meth手法でのクラスタリング return(cutree(hc,k=clsnum)) #クラスターを clsnum個に分割し返す } #関数:クラスターの評価(Entropy, Purity) evalhclust <- function(result, answer){ ct <- table(answer, result) #クロス表の作成 cat("Entropy: ", calcEntropy(ct), "\n") #エントロピー cat("Purity : ", calcPurity(ct), "\n") #純度 }
エントロピー・純度 比較。
x <- iris[,1:4] #解析データ:iris 1-4列のデータ #各手法でのクラスタリング hcc.aver <- calchclust(x,clsnum=3,meth="average") #群平均法 hcc.sngl <- calchclust(x,clsnum=3,meth="single") #単連結法 hcc.comp <- calchclust(x,clsnum=3) #完全連結法(Default):"Complete"指定と同じ hcc.ward <- calchclust(x,clsnum=3,meth="ward") #ウォード法 hcc.cntr <- calchclust(x,clsnum=3,meth="centroid") #重心法 hcc.medi <- calchclust(x,clsnum=3,meth="median") #メディアン法 #評価 ans <- iris[,5] # evalhclust(hcc.aver,ans) #群平均法 evalhclust(hcc.sngl,ans) #単連結法 evalhclust(hcc.comp,ans) #完全連結法(Default):"Complete"指定と同じ evalhclust(hcc.ward,ans) #ウォード法 evalhclust(hcc.cntr,ans) #重心法 evalhclust(hcc.medi,ans) #メディアン法
実行結果
> #評価 > ans <- iris[,5] #クラスタリング正解:品種(iris5列目) > evalhclust(hcc.aver,ans) #群平均法 Entropy: 0.1799098 Purity : 0.9066667 > evalhclust(hcc.sngl,ans) #単連結法 Entropy: 0.05095645 Purity : 0.9866667 > evalhclust(hcc.comp,ans) #完全連結法(Default):"Complete"指定と同じ Entropy: 0.2390843 Purity : 0.84 > evalhclust(hcc.ward,ans) #ウォード法 Entropy: 0.2150906 Purity : 0.8933333 > evalhclust(hcc.cntr,ans) #重心法 Entropy: 0.1799098 Purity : 0.9066667 > evalhclust(hcc.medi,ans) #メディアン法 Entropy: 0.1738730 Purity : 0.9133333
Google Group
推薦文献:

- 作者: 新納浩幸
- 出版社/メーカー: オーム社
- 発売日: 2007/11/01
- メディア: 単行本
- 購入: 9人 クリック: 207回
- この商品を含むブログ (29件) を見る

- 作者: 宮本定明
- 出版社/メーカー: 森北出版
- 発売日: 1999/10
- メディア: 単行本
- クリック: 36回
- この商品を含むブログ (8件) を見る

- 作者: 金明哲
- 出版社/メーカー: 森北出版
- 発売日: 2007/10/01
- メディア: 単行本(ソフトカバー)
- 購入: 36人 クリック: 694回
- この商品を含むブログ (64件) を見る